Table 1. Information about the TFs.
| Name |
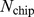
|
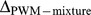
|
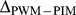
|
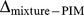
|
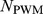
|
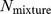
|
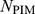
|
| Bap |
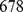
|

|
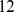
|
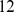
|
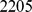
|
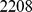
|
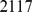
|
| Bin |
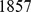
|

|
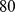
|
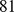
|
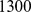
|
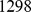
|
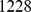
|
| Mef2 |
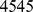
|

|
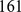
|
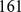
|
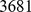
|
|
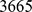
|
| Tin |
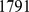
|

|
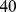
|
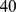
|
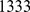
|
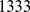
|
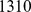
|
| Twi |
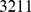
|
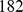
|
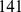
|
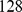
|
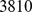
|
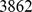
|
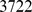
|
| c-Myc |
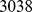
|

|
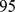
|
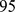
|
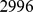
|
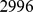
|
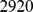
|
| E2f1 |
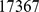
|

|
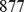
|
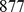
|
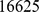
|
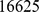
|
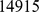
|
| Esrrb |
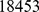
|
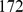
|
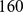
|
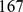
|
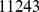
|
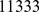
|
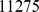
|
| Klf4 |
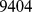
|

|
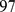
|
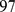
|
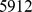
|
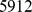
|
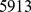
|
| Nanog |
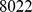
|

|
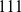
|
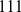
|
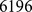
|
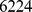
|
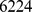
|
| N-Myc |
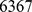
|

|
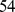
|
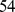
|
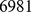
|
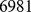
|
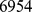
|
| Oct4 |
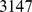
|

|
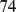
|
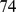
|
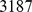
|
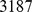
|
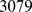
|
| Smad1 |
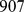
|

|
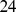
|
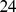
|
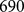
|
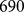
|
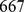
|
| Sox2 |
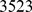
|

|
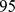
|
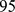
|
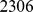
|
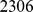
|
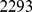
|
| STAT3 |
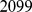
|
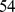
|
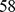
|
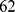
|
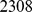
|
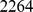
|
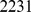
|
| Tcfcp2l1 |
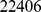
|

|
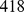
|
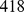
|
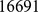
|
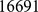
|
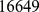
|
| Zfx |
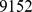
|

|
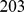
|
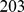
|
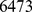
|
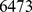
|
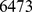
|
| C/EBP-beta |
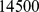
|
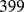
|
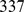
|
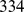
|
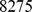
|
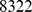
|
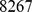
|
| CTCF |
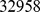
|
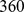
|
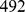
|
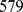
|
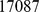
|
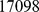
|
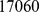
|
| E2f4 |
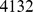
|
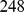
|
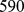
|
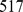
|
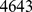
|
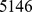
|
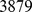
|
| Fosl1 |
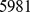
|

|
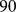
|
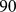
|
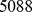
|
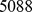
|
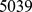
|
| Max |
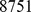
|
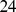
|
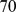
|
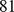
|
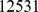
|
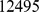
|
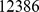
|
| MyoD |
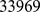
|
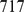
|
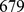
|
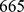
|
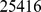
|
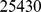
|
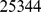
|
| Myog |
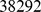
|
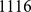
|
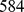
|
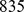
|
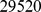
|
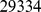
|
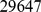
|
| NRSF |
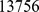
|
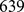
|
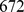
|
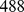
|
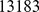
|
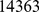
|
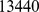
|
| SRF |
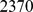
|

|
|
|
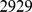
|
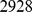
|
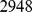
|
| TCF3 |
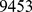
|
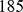
|
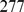
|
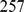
|
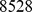
|
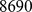
|
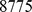
|
| USF1 |
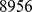
|

|
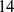
|
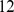
|
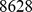
|
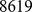
|
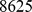
|
For each TF, we show the number 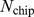 of ChIP sequences retrieved, the numbers
of ChIP sequences retrieved, the numbers 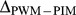 ,
, 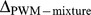 , and
, and 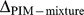 of different ChIP sequences used for training between either two models, and the numbers
of different ChIP sequences used for training between either two models, and the numbers 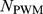 ,
, 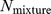 , and
, and 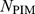 of TFBSs used to learn each model.
of TFBSs used to learn each model.
